在細胞內,核糖體依據承載遺傳資訊的DNA,將20種氨基酸按特定排列順序連接數十至數千個,從而合成蛋白質。近年研究發現,存在一些核糖體難以合成的胺基酸序列。這類胺基酸序列被稱為「難翻譯序列」。這些會導致蛋白質合成中斷的難翻譯序列,對生物而言本是不利的,因此闡明其存在對生物演化產生了何種影響,具有極為重要的意義。
日本大學共同利用機關法人資訊與系統研究機構國立遺傳學研究所的藤原圭吾特命助教與京都產業大學的千葉志信教授等人的研究團隊,發現了細菌共有的難翻譯序列模式,同時證實存在一類能主動利用難翻譯序列發揮作用的特殊蛋白質群。
研究團隊首先通過系統性突變分析,確定出當胺基酸序列中含有精胺酸-甘胺酸-脯胺酸-脯胺酸(RGPP)或精胺酸-丙胺酸-脯胺酸-脯胺酸(RAPP)時,容易形成難翻譯序列。然後通過對網羅整個細菌界的遺傳資訊進行全面分析,發現RGPP序列在細菌界中出現的頻率最低。此外,研究團隊重點關注了羧基末端附近大量存在RAPP或RGPP序列的放線菌,通過生物資訊學分析證實,這些蛋白質具有被認為可用於監測細胞內外環境並幫助生物體適應環境的未知的生理功能。
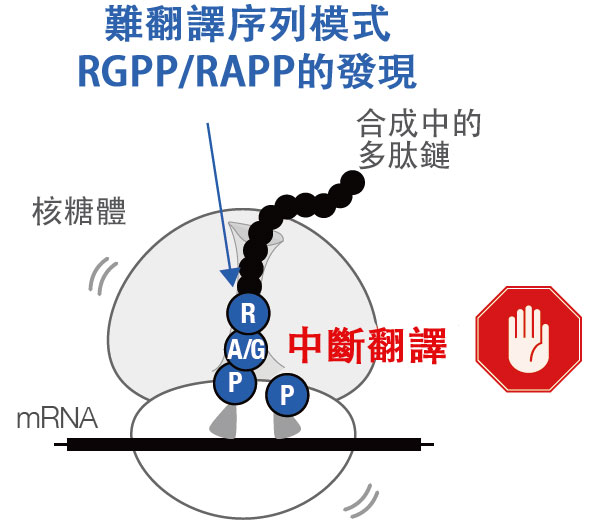
核糖體通過翻譯傳訊RNA(mRNA)來合成蛋白質。研究發現,在許多細菌中,存在會導致核糖體蛋白質合成中斷的難翻譯序列的共同模式,並探究了其功能。
此次研究成果為理解遺傳資訊的進化、基因表現及翻譯的分子機制提供了基礎理論依據。同時有望為利用細菌及微生物生產有用化合物的「生物製造」以及抗生素研發提供重要助力。(TEXT:中條將典)
原文:JSTnews 2026年3月號
翻譯:JST客觀日本編輯部
【論文資訊】
期刊:The EMBO Journal
論文:Evolutionary Adaptation of Bacterial proteomes to Translation-Impeding Sequences
DOI:10.1038/s44318-025-00651-6